Bugün öğrendim ki: Kök hücre nakliyle HIV'in tedavisi mümkün. Ancak bir sorun var: Bu yöntem sadece hayati tehlike arz eden kan kanseri olan hastalar için kullanıldı.
Etik
Yazılı bilgilendirilmiş onam, Charité Universitätsmedizin Berlin yerel Etik Kurulu ile yapılan görüşmenin ardından hasta B2'den alınmıştır. Hasta B2'den alınan biyolojik örnekler, Charité Universitätsmedizin Berlin Etik Kurulu uyarınca (referans numarası EA4/261/23) araştırma amaçlı kullanılmıştır. ART'yi (antiretroviral tedavi) sonlandırma kararı, hasta B2 tarafından bağımsız olarak alınmıştır. HIV negatif kan bağışçıları ve HIV ile yaşayan bireylerin dahil olduğu kontrol grubu katılımcıları, Charité Universitätsmedizin Berlin ve Hamburg-Eppendorf Üniversite Tıp Merkezi'nde onaylanmış etik protokoller çerçevesinde (Charité Universitätsmedizin Berlin Etik Kurulu, referans numaraları EA2/077/23 ve EA4/255/23; ve Ärztekammer Hamburg, referans numarası PV4780) kaydedilmiştir. HIV enfeksiyonu olmaksızın allo-SCT (allojenik kök hücre nakli) alan hastalardan alınan biyolojik örnekler, daha önceki bir çalışmanın57 parçası olarak toplanmıştır. Tüm katılımcılardan yazılı bilgilendirilmiş onam alınmış ve çalışmalar İyi Klinik Uygulamalar'a uygun olarak yürütülmüştür.
Numune işleme
Kan örnekleri, daha önce oluşturulmuş protokoller58 uyarınca toplanmış ve işlenmiştir. Serum ve plazma örnekleri -80 °C'de saklanmıştır. PBMC'ler (periferik kan mononükleer hücreleri), yoğunluk gradyanı santrifüjü (1,077 g ml–1 Pancoll, PAN Biotech) ile izole edilmiş ve sıvı azotta saklanmadan önce %10 DMSO içeren fetal sığır serumu içinde dondurularak korunmuştur.
HIV-1 RNA plazma viral yükünün tespiti ve kantifikasyonu
Plazma viral yükü, 2019 Aralık ayına kadar, 25 kopya/ml alt tespit limitine (LLOD) sahip m2000sp otomatik nükleik asit ekstraksiyonu ve m2000rt gerçek zamanlı PCR döngüleyici kullanan Abbott RealTime HIV-1 testi (2G31-090) ile ölçülmüştür. 2019 Aralık ayından itibaren, Alinity m platformunda 14,0 kopya/ml LLOD değerine sahip Abbott Alinity m HIV-1 AMP Kiti (8N45-090) kullanılmıştır. 2023 Eylül ayından sonra HIV-1 RNA test ve kantifikasyonu Cobas HIV-1 testi (Roche) kullanılarak yapılmıştır. Bu testin analitik duyarlılığı (≥%95 isabet oranı ile LOD) 14,2 kopya/ml'dir ve kantifikasyon için doğrusal aralık 20−1 × 10^7 kopya/ml'dir.
Kimerizm
Kimerizm analizleri, floresan etiketli primerler ve DNA fragman analizi kullanılarak PCR yoluyla donör ve alıcı allellerinin kısa tandem tekrarlar (STR'ler) üzerinde ayırt edilmesine dayanmıştır. Bilgilendirici STR lokuslarını tespit etmek için başlangıç genotiplendirmesi, hasta ve donörden veya greftten alınan EDTA'lı periferik kan kullanılarak yapılmıştır. Nakilden sonra kimerizm, kemik iliği ve periferik kan örneklerinde analiz edilmiştir. CD34+ (kemik iliğinden) ve CD3+ (periferik kandan) hücrelerin izolasyonu, standart MACS tekniği (Miltenyi Biotec) kullanılarak gerçekleştirilmiştir. DNA, üreticinin önerdiği standart bir DNA ekstraksiyon kiti (QIAamp; Qiagen) kullanılarak ekstrakte edilmiştir. PCR reaksiyonu, 16 farklı lokusun eş zamanlı amplifikasyonu için floresan etiketli primer çiftleri içeren ticari bir AmpFℓSTR Identifier PCR Amplifikasyon Kiti (Thermo Fisher Scientific) kullanılarak yürütülmüştür. Kimerizmin kantifikasyonu için, eğri altındaki alanlar GeneMapper (v.3.7) yazılımı (Thermo Fisher Scientific) kullanılarak hesaplanmıştır. Yöntemin duyarlılığı %1'dir.
Tüm ekzom dizileme
Donör ve alıcıdan alınan genomik germ hattı DNA'sı bir Qubit Florometre kullanılarak kantifiye edilmiş ve DNA bütünlüğü TapeStation (Agilent) kullanılarak değerlendirilmiştir. Toplam 200 ng girdi genomik DNA (gDNA), Agilent SureSelect Enzimatik Fragmantasyon Kiti (Agilent) kullanılarak 25 dakika boyunca enzimatik olarak fragmanlara ayrılmıştır. Kütüphane hazırlığı, üreticinin önerileri doğrultusunda AMPure XP/Streptavidin Boncukları (Agilent) ve Agilent Human All Exon v8 zenginleştirme yemleri (5191-6875, Agilent) içeren Agilent SureSelect XT HS2 DNA Reaktif Kiti kullanılarak gerçekleştirilmiştir. Kütüphaneler, Qubit konsantrasyon ölçümlerine ve TapeStation boyut dağılımlarına dayanarak eşmolar konsantrasyonlarda havuzlanmıştır. Havuzun yükleme konsantrasyonu bir qPCR testi (Roche) kullanılarak belirlenmiştir. Kütüphaneler, örnek başına 50 milyon okuma (yaklaşık 75× kapsama) hedefiyle PE100 dizileme modu kullanılarak Illumina NovaSeq X Plus platformunda dizilenmiştir.
Aday miHA'ların tahmini
Donör ve alıcı tüm ekzom dizileme verilerinden sistematik miHA (küçük histokompatibilite antijeni) keşfi için kullanılan süreç, önceki bir çalışmadan18 uyarlanmış ve dizileme okumaları BWA ile hg38 referans genomu ile hizalanmıştır. Germ hattı varyant çağırma ve fonksiyonel SNP anotasyonu sırasıyla Deepvariant59 ve Funcotator (GATK4) kullanılarak gerçekleştirilmiştir. Donör ve alıcıdan gelen ekzonik eş anlamlı olmayan varyantlar karşılaştırılmış ve sadece alıcıda bulunan uyumsuz varyantlar tanımlanmıştır. GVL filtresi daha önce yayınlanmıştır18 ve 650 gen içeren AML filtresi ile hematopoetik filtreden oluşur. CD4 T hücresi filtresi, sağlıklı donör PBMC veri setlerinde CD4 T hücrelerinin %5'inden fazlasında ifade edilen 7.208 gen temel alınarak oluşturulmuştur (https://atlas.fredhutch.org/nygc/multimodal-pbmc/)60. GVL ve CD4 T hücresi filtrelerindeki genlerde bulunan uyumsuz varyantlar seçilmiş ve varyantları kapsayan tüm olası k-merler oluşturulmuştur. Ayrıca, kadın-erkek nakillerinde allo-tanımanın ek hedefleri olarak erkek spesifik Y kromozomu bölgesindeki genlerden (dokuz gen) kaynaklanan olası k-merler oluşturulmuştur. Tüm k-merler, hem donörün hem de alıcının ekzomlarından elde edilen özel in silico proteomlara karşı sıralı olarak BLAST edilmiştir ve ilişkisiz doku bölgelerinde bulunan tüm k-merler atılmıştır. Kalan benzersiz k-merler, bağlayıcıları tanımlamak için %0,5 tahmin sıralaması eşiği kullanılarak, hastaya özgü HLA sınıf I allelleri ile bağlanma afinitesini tahmin etmek için HLAthena61'ye tabi tutulmuştur.
Plazmada antiretroviral ilaç taraması
Plazmadaki HIV ilaç seviyeleri, amprenavir, darunavir, efavirenz, indinavir, lopinavir, maraviroc, nelfinavir, nevirapin, raltegravir, ritonavir, saquinavir, etravirin, elvitegravir, dolutegravir, tipranavir, tenofovir ve emtrisitabin varlığını kontrol etmek için 25 ng ml–1 plazma LLOD değerine sahip, ters fazlı LC–MS/MS tabanlı çoklu reaksiyon izleme modunda kurum içi bir yöntemle ölçülmüştür.
Mukoza hücresi izolasyonu
Mukoza mononükleer hücreleri (MMC'ler), 16 duodenal veya 20 ileal biyopsiden 1 mM EDTA ile muamele ve kolajenaz tip II (Sigma) ile sindirim, ardından Percoll gradyan santrifüjü62 yoluyla izole edilmiştir. Akış sitometrisi panellerinde kullanılan antikor klonlarının, kolajenaz ile muamele edilmiş hücrelerin analizi için uygun olduğu test edilmiştir. Fenotipleme için şu antikorlar kullanılmıştır: anti-CD3-PerCP (SK7; BD, 1:20 seyreltme); anti-CD4-Pacific Blue (RPA-T4; BD, 1:25 seyreltme); anti-CD19-PE-Cy7 (SJ25C1; BD, 1:50 seyreltme); anti-CD45-FITC (HI30; eBioscience, 1:25 seyreltme); anti-CD326-PE-Cy7 (9C4; BioLegend, 1:50 seyreltme); ve anti-HLA-DR-PE (LN3; eBioscience, 1:10 seyreltme). CD45+CD4+ hücreleri, FACSJazz sitometresi (BD) kullanılarak akış sıralaması yoluyla anti-CD4-FITC (RPA-T4; BD, 1:20 seyreltme), anti-CD45-V500 (HI30; BD, 1:50 seyreltme) ve anti-CD326-PE-Cy7 (1:50 seyreltme) kullanılarak MMC'lerden saflaştırılmıştır.
Toplam HIV DNA'sı
Toplam proviral HIV-1 DNA'sının tespiti için gDNA, QIAamp DNA Blood Mini Kit (Qiagen) veya Maxwell RSC Whole Blood DNA Kit (Promega) kullanılarak periferik kandan izole edilmiştir. PCR, daha önce tarif edildiği gibi1 env ve long-terminal-repeat (LTR) bölgelerini hedefleyen iki bağımsız reaksiyonu içermiştir.
Gastrointestinal biyopsi örneklerinde ve PBMC'lerde toplam HIV-1 DNA'sı
Proviral HIV DNA'sı, duodenum veya ileumun lamina propriasından izole edilen mononükleer hücrelerde ve duodenumdan alınan CD45+ CD4 hücrelerinde, daha önce oluşturulmuş protokoller1,57 uyarınca PCR ile değerlendirilmiştir. Dijital PCR (dPCR) ile ek rezervuar kantifikasyonu için, MMC'lerin dört alikotu 200 µl PBS içinde yeniden süspanse edilmiş ve DNA, QIAmp DNA Mini Kit (Qiagen) kullanılarak izole edilmiştir. Genomik verimi kantifiye etmek için, PBMC eluatı için 20 ng ve her bir gastrointestinal biyopsi eluatı için 5 µl üzerinde RPP30 testi22 kullanılarak dPCR yapılmıştır. Potansiyel HIV rezervuarlarının tespiti için, PBMC'lerden elde edilen 500 ng gDNA veya gastrointestinal biyopsiden alınan dört alikottan 20 µl, ikili test ile dPCR yoluyla toplam HIV DNA'sı (RU5)63 için test edilmiştir. Bağırsak biyopsi örneklerinden ve PBMC eluatından dPCR rezervuar ölçümleri QIAcuity One 5-plex (Qiagen) üzerinde gerçekleştirilmiştir.
Üçlü IPDA
CD4 hücreleri, 20 ml periferik kandan pozitif seleksiyon (Dynabeads CD4, Thermo Fisher Scientific) yoluyla izole edilmiştir. CD4 hücresi DNA'sı üç alikot halinde izole edilmiştir. Kesme faktörü ve genomik verim, 20 ng DNA şablonlarında RPP30 testi22 kullanılarak değerlendirilmiştir. Üçlü IPDA, toplam HIV DNA'sını (RU5)63 ve sağlam proviral HIV DNA'sının kantifikasyonunu (paketleme sinyali (PSI), Env ve etiketlenmemiş Env hipermutasyon probu)21, kuyu başına en az üçlü test ile 500 ng şablonlarda içerir. Tüm dPCR testleri QIAcuity One 5-plex (Qiagen) üzerinde gerçekleştirilmiştir.
Q4ddPCR
CD4 T hücreleri, üreticinin talimatlarına göre CD4 T Hücresi İzolasyon Kiti (Miltenyi Biotec) kullanılarak örneklerden izole edilmiştir. gDNA daha sonra QIAamp DNA Mini Kit (Qiagen) kullanılarak ekstrakte edilmiştir. Kuyu başına 750 ng'a kadar DNA, problar için süper karışım (dUTP yok) (Bio-Rad) ve özel bir primer-prob karışımı ile birleştirilmiştir. Bu karışım, değişen nihai konsantrasyonlarda etiketlenmemiş bir hipermutant Env probu ile birlikte dört floresan etiketli dahili hidroliz probu içermiştir. Primer ve prob dizileri, florofor etiketlemede değişiklikler yapılarak yayınlanmış dizilere dayandırılmıştır21,64. Her hedef için diziler şöyledir: Env: primer (0,225 µM): ileri AGTGGTGCAGAGAGAAAAAAGAGC, geri GTCTGGCCTGTACCGTCAGC, prob (0,0625 µM): /5-VIC-CCTTGGGTTCTTGGGA-MGBNFQ, hedefteki hipermutasyonların ayrımı için etiketlenmemiş hipermutant prob: CCTTAGGTTCTTAGGAGC-MGBNFQ; PSI: primer (0,9 µM): ileri CAGGACTCGGCTTGCTGAAG, geri GCACCCATCTCTCTCCTTCTAGC, prob (0,25 µM): /56-FAM/TTTTGGCGTACTCACCAGT-MGBNFQ); Gag: primer (0,9 µM): ileri ATG TTT TCA GCA TTA TCA GAA GGA, geri TGC TTG ATG TCC CCC CAC T, prob (0,25 µM): /5Cy5/CCACCCCAC/TAO/AAGATTTAAACACCATGCTAA/3IAbRQSp/); Pol: primer (0,9 µM): ileri GCA CTT TAA ATT TTC CCA TTA GTC CTA, geri CAA ATT TCT ACT AAT GCT TTT ATT TTT TC, prob (0,25 µM): /5ATTO590N/AAGCCAGGAATGGATGGCC/3IAbRQSp/). Env ve PSI probları hariç (bunlar bir minor groove binder (Thermo Fisher Scientific) içeriyordu), primerler ve problar Integrated DNA Technologies'den satın alınmıştır. Reaksiyonlar, kuyu başına toplam 20 µl hacimde dört adede kadar replika kuyuda gerçekleştirilmiştir. Damlacıklar otomatik bir damlacık üreticisi (Bio-Rad) ile oluşturulmuştur. Termal döngü, 2 °C'lik bir rampa hızı ile, 10 dakika boyunca 95 °C'de başlangıç denatürasyonunu, ardından 60 döngüyü (döngü başına 94 °C'de 30 saniye ve 55 °C'de 1 dakika) ve 4 °C'de inkübasyondan önce 98 °C'de 10 dakikalık son adımı içermiştir. Damlacıklar bir QX600 Damlacık Okuyucu (Bio-Rad) üzerinde okunmuştur. Ertesi gün, DNA kesilmesini düzeltmek ve daha önce tarif edildiği gibi21 hücre eşdeğerlerini hesaplamak için Paralel RPP30 testleri kullanılmıştır. 7.500'den az damlacık veya 40.000'den az hücre eşdeğeri içeren örnekler dışarıda bırakılmıştır. Pozitif ve negatif kontroller ikili olarak gerçekleştirilmiştir. Verileri toplamak ve analiz etmek için QX Manager Software Standard Edition (v.2.1) kullanılmıştır.
Viral çoğalma testi
Sınırlı seyreltme virüs kültürü testleri için, CD4 T hücreleri REAlease CD4 MicroBead Kiti (Miltenyi) kullanılarak PBMC'lerden ayrılmış, 1:1 boncuk/hücre oranında anti-CD3/CD28 kaplı mikroboncuklar ve 24 saat boyunca 30 U ml–1 IL-2 (Peprotech) ile aktive edilmiş ve 100 U ml–1 IL-2 varlığında SupT1-R5 hücreleri veya CD4 lenfoblastları ile %10 ısıl işlem görmüş fetal buzağı serumu (Sigma), 100 U ml–1 penisilin ve 100 µg ml−1 streptomisin (her ikisi de Biochrom'dan) içeren RPMI 1640 GlutaMAX hücre kültürü ortamında ortak kültüre edilmiştir. Kullanılan lenfoblastlar, CCR5 vahşi tip bir donörün PBMC'lerinden, 1 µg ml–1 fitohemaglütinin (Sigma) ve 100 U ml–1 IL-2 ile 2 gün boyunca aktivasyon ve ardından CD8 ve CD56 hücrelerinin tüketilmesi (Miltenyi) ile hazırlanmıştır. Kültür süpernatantları her 2 veya 3 günde bir toplanmış ve taze ortam eklenmiştir. Süpernatantlar, üreticinin protokolüne göre HIV-1 p24 ELISA testi (Sino Biological) ile HIV-1 çekirdek proteini p24 üretiminin kantitatif ölçümü ile virüs üretimi analizi yapılana kadar -80 °C'de saklanmıştır. Bulaşıcı HIV birimleri, sırasıyla <0,05 (ilk zaman noktası, tedavinin kesilmesinden 62 ay sonra) veya 0,006 (ikinci zaman noktası, tedavinin kesilmesinden 78 ay sonra) milyon CD4 T hücresi başına bulaşıcı birim tahmini LLOD ile IUPMStats (v. 1.0) hesaplayıcısı kullanılarak kantifiye edilmiştir65.
CCR5 genotipleme ve haplotipleme
gDNA, QIAamp DNA Mini Kit (Qiagen) kullanılarak heparinize periferik kandan, tırnak örneklerinden veya saç köklerinden ekstrakte edilmiştir. DNA daha sonra kromozom 3p21.31 üzerindeki 805'ten 988'e kadar olan nükleotitler arasındaki Δ32 bölgesini kapsayan CCR5 geni için oligonükleotitlerle PCR amplifikasyonuna tabi tutulmuştur (erişim no: NM_000579.4). Beklenen fragmanlar, CCR5 vahşi tipi için 184 bp ve CCR5Δ32 varyantı için 152 bp'dir. Her iki varyantı da içeren örneklerde uyumsuz heterodupleks DNA oluşmuştur. Haplotipleme, daha önce tarif edilen yöntemlere23,66 göre gerçekleştirilmiştir. 25 µl'lik PCR reaksiyon karışımı 1 µl DNA (reaksiyon başına 25–100 ng'a karşılık gelir), 5 µl 5× OneTaq standart reaksiyon tamponu, 0,5 µl dNTP'ler (10 mM), 0,5 µl ileri ve geri primerler (10 µM) (CCR5 ileri GACGAGAAAGCTGAGGGTAAGA, CCR5 geri TAACCGTCTGAAACTCATTCCA; CCR2 ileri TACGGTGCTCCCTGTCATAAA; CCR2 geri TGGAAAATAAGGGCCACAGAC) ve 0,125 µl OneTaq DNA polimeraz (NEB, M0480S) içermiştir. Termal döngü koşulları şöyledir: 94 °C'de 30 saniye başlangıç denatürasyonu; 94 °C'de 15 saniye, 55 °C'de 15 saniye ve 68 °C'de 90 saniye (CCR5 amplifikasyonu için) veya 30 saniye (CCR2 amplifikasyonu için) 30 döngü; ardından 68 °C'de 5 dakika son uzama. Beklenen PCR ürün boyutları CCR5 için 1.388 bp ve CCR2 için 504 bp'dir. Sanger dizilemesi için geri primerler kullanılmıştır (Eurofins Genomics). CCR5'in promotör bölgesindeki (A29G, G208T, G303A, T627C, C630T, A676G ve C927T) ve CCR2'nin kodlayıcı bölgesindeki (V64I) polimorfizmler SnapGene kullanılarak belirlenmiştir.
HIV duyarlılık testi
HIV negatif bireylerden alınan PBMC'ler, RPMI 1640 hücre kültüründe son 2 gün boyunca 100 U ml–1 IL-2 (Merck) varlığında 3 µg ml–1 fitohemaglütinin (Merck) ile 3 gün boyunca aktive edilmiştir. Hücreler yıkanmış ve 100 U ml–1 IL-2 ile desteklenmiş ortamda 0,01 enfeksiyon çokluğu ile HIV-1 suşu HTLVIIIB, Ba-L veya SF162 ile ya da Alman HIV-1 Serokonvertör Kohortu'ndan67 CXCR4-tropik (izolat 1.2), CCR5-tropik (izolat 2) veya dual X4/R5-tropik (izolat 1.1) birincil hasta izolatı ile ml başına 10^6 olacak şekilde kültüre edilmiştir. Ortak reseptör kullanımı, Geno2Pheno[co-receptor]68 kullanılarak %20'lik bir belirsizlik eşiği ile HIV-1 popülasyon dizilerinden genotipik olarak doğrulanmıştır. HIV-1 popülasyon dizileri daha önce tarif edildiği gibi69, ancak Nextera XT DNA Kütüphane Hazırlama Kiti ve MiSeq Reaktif Kiti v.3 (Illumina) kullanılarak belirlenmiştir. Hücresiz ortamda seyreltilmiş viral stoklar arka plan kontrolü, sadece hücreler yalancı (mock) kontrol ve hücresiz virüs süspansiyonları arka plan düzeltmeleri için kontrol olarak kullanılmıştır. Süpernatantlar belirtildiği gibi hücre kültürlerinden ve hücresiz kontrollerden uzaklaştırılmış, taze ortamla değiştirilmiş ve daha önce tarif edildiği gibi70 gerçekleştirilen kurum içi geliştirilmiş HIV-1 p24 antijen yakalama ELISA ile HIV-1 çekirdek proteini p24 üretiminin kantitatif ölçümü ile viral replikasyon analizi yapılana kadar -80 °C'de saklanmıştır. Kısaca, 96 kuyulu mikrotitre plakaları (Maxisorp, Thermo Scientific), bikarbonat tamponunda (pH 9.6) optimize edilmiş seyreltmede saflaştırılmış AG3.0 antikoru ile kaplanmış ve 4 °C'de gece boyunca inkübe edilmiştir. Plakalar daha sonra %0,05 Tween-20 içeren PBS (PBST) ile üç kez yıkanmış ve 37 °C'de nemli, %5 CO2 inkübatöründe 45 dakika boyunca bloklama tamponu (%2 süt tozu, PBS (PM)) ile inkübe edilmiştir. Örnekler, bloklama tamponu artı %0,05 Tween-20 (PMT) içinde 1:100, 1:200 veya 1:500 oranında seyreltilmiştir. Kantifikasyon standardı olarak, daha önce ticari bir ELISA (HIV-1 p24 antijen ELISA, Aalto Bio Reagents) ile 43,42 p24 ng ml–1 içerdiği belirlenen bir HIV-1 virüs lizatı da plaka boyunca titre edilmiştir. 37 °C'de 45 dakikalık inkübasyondan sonra, plakalar PBST ile üç kez yıkanmış ve PMT içinde 1:10.000 seyreltmede kurum içi havuzlanmış insan anti-HIV-1 serumları ile inkübe edilmiştir. 37 °C'de 45 dakikalık inkübasyondan sonra plakalar PBST ile üç kez yıkanmış ve PMT içinde 1:1.000 seyreltilmiş keçi anti-insan IgG–peroksidaz konjugatı (Sigma-Aldrich) tüm kuyulara eklenmiştir. Son olarak, plakalar üç kez yıkanmış ve kuyu başına 100 μl 3,3′,5,5′-tetrametilbenzidin (Sigma-Aldrich) substratı ile inkübe edilmiştir. 5–10 dakika sonra istenen renk gelişimi sağlanmış ve reaksiyon, ELISA mikroplaka okuyucuda (Infinite 200, Tecan) 450'ye karşı 620 nm'de optik yoğunluğu ölçmeden önce 1 M H2SO4 eklenerek durdurulmuştur. 12. günde hücreler toplanmış ve QIAamp DNA Blood Mini Kit (Qiagen) kullanılarak DNA izole edilmiştir. Kantitatif provirüs PCR, daha önce tarif edildiği gibi71 CFX96 cihazı (Bio-Rad) üzerinde yürütülmüştür.
T hücrelerinin fenotipleme karakterizasyonu
CCR5 analizleri için örnekler, toplandıktan sonra 5 dakika içinde işlenmiştir. Heparinize kan, oda sıcaklığında 15 dakika boyunca antikorlarla inkübe edilmiş ve eritrositlerin lizisinden sonra hücreler hemen akış sitometrisi ile analiz edilmiştir. Şu antikorlar kullanılmıştır: anti-CD3-APC-H7 (SK7; BD Biosciences, 1:100); anti-CD4-PerCPCy5.5 (SK3; BD, 1:25); anti-CD8-Pacific Blue (RPA-T8; BD, 1:200); anti-CD14-PE-Cy7 (61D3, eBioscience, 1:200); anti-CD19-PE-Cy7 (1:100); CD45RO-VioGreen (UCHL-1; Miltenyi, 1:100); ve anti-CCR5-APC (2D7; BD, 1:10). Klon 2D7, 32-bp silinme 2D7 bağlanma bölgesinin kaybına yol açtığından, CCR5'in vahşi tipini tanır ancak Δ32 varyantını tanımaz. CD4 T hücrelerinde CCR5 ifade yoğunluğu, CCR5 CD4 T hücrelerinin CCR5 MFI değerinin, karşılık gelen floresans-eksi-bir kontrolü ile elde edilen toplam CD4 T hücrelerinin MFI değerine bölünmesiyle değerlendirilmiş ve MFI oranı olarak ifade edilmiştir. Tam kanda CD4 T hücresi kompozisyonunun analizi, daha önce tarif edildiği gibi72 şu antikorlar kullanılarak gerçekleştirilmiştir: anti-CD4-PerCPCy5.5 (1:35); anti-CD31-PE (WM59; BD, 1:35); anti-CD45RO-APC (UCHL-1; BD 1:450); ve anti-CD62L-FITC (Dreg-56; BD, 1:70). CD4+ ve CD8+ T hücrelerinin mutlak sayıları, üreticinin protokolüne göre TruCount tüpleri ve CD3/CD4/CD8 TritTest (BD) kullanılarak belirlenmiştir. Veriler FACSCanto II sistemi (BD) üzerinde toplanmış ve FlowJo yazılımı (v.10.10.0; BD) ile analiz edilmiştir.
V3 döngüsü dizileme ve HIV-1 ortak reseptör kullanım tahmini
V3 döngü bölgesini içeren PCR ürünleri, HIV6945A ve HIV7626B primerleri kullanılarak oluşturulmuştur. Yeni nesil dizileme, Vela Diagnostics'in kütüphane hazırlama, emülsiyon PCR ve dizileme reaktifleri kullanılarak IonTorrent PGM platformunda yarı iletken dizileme temelinde gerçekleştirilmiştir. Ortaya çıkan diziler geno2pheno[454] önişlemcisi kullanılarak ön işleme tabi tutulmuş ve geno2pheno[454] internet platformuna yüklenmiştir25. Sonuçlar %2 popülasyon kesme değerleri ve %3,5 yanlış pozitif oranı kullanılarak yorumlanmıştır73.
Filogenetik ağaç oluşturma
Diziler ve filogenetik ağaç, daha önce tarif edilen yöntemler2 kullanılarak oluşturulmuştur. Kısaca, diziler MUSCLE (v.3.8.155)74 kullanılarak hizalanmıştır. Los Alamos HIV Dizi Veritabanı'ndan (http://www.hiv.lanl.gov/) iki HIV-1 alt tip D izolatı dış grup olarak dahil edilmiştir. Laboratuvar izolatlarından (HTLVIIIB, Ba-L ve SF162) ve Alman HIV-1 Serokonvertör Çalışması izolatlarından (izolat 1.1, 1.2 ve 2) referans diziler de dahil edilmiştir67. Filogenetik analiz raxmlGUI (v.2.0)75 kullanılarak gerçekleştirilmiştir. Maksimum olabilirlik filogenisi FigTree (v.1.4.4) kullanılarak görselleştirilmiştir.
İnsan plazması RNA kaynaklı tek genom dizileme
Plazma RNA'sı, DNase I sindirim adımı (Qiagen) dahil edilerek MinElute Virus Spin Kit (Qiagen) kullanılarak izole edilmiştir. cDNA, SuperScript III ters transkriptaz (Thermo Fisher) kullanılarak antisense primer envB3out (5′-TTGCTACTTGTGATTGCTCCATGT) ile sentezlenmiş ve ardından RNase H (Thermo Fisher) ile işleme tabi tutulmuştur. Ortaya çıkan env cDNA daha sonra daha önce oluşturulmuş yöntemlere76,77 dayalı bir protokol kullanılarak amplifiye edilmiştir. PCR amplifikasyonu, Phusion Hot Start Flex DNA polimeraz (New England Biolabs) ile gerçekleştirilmiştir. İlk PCR turu 98 °C'de 45 saniye, ardından 98 °C'de 15 saniye, 55 °C'de 30 saniye ve 72 °C'de 4 dakika olmak üzere 35 döngü ve 72 °C'de 15 dakikalık son uzama ile yapılmıştır. İlk tur PCR ürününün 1 µl'lik bir alikotu, benzer döngü koşullarını takip eden ikinci tur PCR için şablon görevi görmüştür: 98 °C'de 45 saniye, 45 döngü 98 °C'de 15 saniye, 55 °C'de 30 saniye ve 72 °C'de 4 dakika, 72 °C'de 15 dakika ile biter. Saflaştırılmış PCR ürünleri Sanger dizilemesine tabi tutulmuş ve dizi verileri Geneious yazılımı (Dotmatics) kullanılarak analiz edilmiştir.
Yalancı virüs üretimi
Yalancı virüsler, daha önce bildirildiği gibi78 otolog hasta yalancı virüsleri B2, Ba-L_26 ve YU-2'yi üretmek için HEK293T hücrelerinde hazırlanmıştır. Tek genom dizilemesinden türetilen env'den yalancı virüs B2-B7'yi oluşturmak için, ilgili env dizisine sahip bir ifade plazmidi TWIST Bioscience'tan sipariş edilmiştir.
Nötralizasyon ve bağlanma testleri için serum ve plazma IgG izolasyonu
Serum ve plazma örnekleri başlangıçta 56 °C'de 40 dakika ısıl işlem görmüş ve ya doğrudan nötralize edici aktivite değerlendirmesi için kullanılmış ya da IgG'yi izole etmek için Protein G Sepharose boncukları (GE Life Sciences) ile 4 °C'de gece boyunca inkübe edilmiştir. Bağlı antikorlar, 0,1 M glisin (pH 3.0) kullanılarak boncuklardan elüe edilmiş ve ardından 1 M Tris (pH 8.0) ile nötralize edilmiştir. Daha sonra tampon PBS ile değiştirilmiş ve antikorlar Amicon 30 kDa santrifüj filtre üniteleri (Millipore) kullanılarak konsantre edilmiştir. Saflaştırılmış IgG örnekleri deneylerde kullanılana kadar 4 °C'de saklanmıştır.
Anti-gp120 ve anti-gp140 ELISA
Yüksek bağlanmalı 96 kuyulu ELISA plakaları (Corning), PBS içindeki saflaştırılmış Env proteinleri His-etiketli alt tip B YU2 trimerik gp140 ve monomerik gp120 ile gece boyunca kaplanmıştır (K. de la Rosa'dan hediye). PBST ile yıkandıktan sonra plakalar 1 saat boyunca %2 BSA (bloklama solüsyonu) ile bloklanmış, yıkanmış ve %2 BSA ile 1:5 oranında seri seyreltilmiş plazma ile (1:10 başlangıç seyreltmesi) inkübe edilmiştir. Yıkamadan sonra, keçi anti-insan IgG–peroksidaz konjugatı (1:10.000, Invitrogen) ve 3,3′,5,5′-tetrametilbenzidin (Sigma-Aldrich) substratı plakalara eklenmiştir. Deneyler, 450 nm'de ölçülen absorbans ile bir mikroplaka absorbans okuyucu kullanılarak gerçekleştirilmiştir. Tüm plazmalar, en az iki bağımsız deneyde ikili olarak test edilmiştir.
Nötralizasyon testleri
Nötralizasyon testleri daha önce tarif edildiği gibi78 gerçekleştirilmiştir. Kısaca, plazma veya saflaştırılmış IgG örneklerinin (3BNC117, VRC01, 1–18, N49P7, VRC07-523-LS, 8ANC195, 10–1074, PGDM 1400, PG16, SF12, 10E8 ve MG053, başlangıç konsantrasyonu 20 µg ml–1) seri seyreltmeleri, 37 °C'de 1 saat boyunca yalancı virüslerle inkübe edilmiştir. Daha sonra 10 µg ml–1 DEAE dekstran ile desteklenmiş 250 µl ortam içeren 96 kuyulu bir plakaya kuyu başına 10^4 hücre yoğunluğunda TZM-bl hücreleri eklenmiştir. %5 CO2 ortamında 37 °C'de 2 gün inkübasyondan sonra 150 µl kültür süpernatantı uzaklaştırılmış ve 100 µl lusiferaz substratı eklenmiştir. Lüminesans, kısa bir 2 dakikalık inkübasyonun ardından bir lüminometre ile ölçülmüştür. Bağıl lüminesans birimlerini (RLU'lar) belirlemek için enfekte olmayan TZM-bl hücrelerinden gelen arka plan lüminesansı çıkarılmıştır. İnhibitör konsantrasyonu (IC50) ve yarı maksimum inhibitör seyreltme (ID50) değerleri, virüs kontrolü ile karşılaştırıldığında %50 inhibisyon elde etmek için gereken antikor veya IgG konsantrasyonlarına ve plazma seyreltmelerine göre hesaplanmıştır. Plazma veya izole edilmiş IgG örneklerinin spesifik olmayan aktivitesini test etmek için, murin lösemi virüsüne dayalı yalancı tiplendirilmiş virüsler dahil edilmiştir. Tüm örnekler ikili olarak test edilmiştir. Biyolüminesans, bir lusiferin/lizis tamponu (MgCl2, ATP, koenzim A, IGEPAL ve d-lusiferin'den oluşur) kullanılarak değerlendirilmiştir. Lüminesans bir lüminometre (Berthold TriStar2S) ile ölçülmüştür. Veriler Microsoft Excel for Mac (v.14.7.3) kullanılarak analiz edilmiştir. İstatistiksel analiz GraphPad Prism (v.9.3.1) kullanılarak gerçekleştirilmiştir.
Virüse özgü tam kan stimülasyonu
Heparinize venöz kan, HIV'in Gag, Pol, Nef veya Env proteininden (hepsi jpt Technologies), EBV'nin BZLF1, EBNA-1 veya LMP1 proteininden (hepsi Miltenyi Biotec), CMV'nin pp65 (jpt) veya IE-1'inden (Miltenyi) veya HHV-6'nın U90 proteininden (jpt) kaynaklanan 11 amino asit örtüşmeli 15-mer dizilerden oluşan peptit karışımları ile stimüle edilmiştir. Bunun için 1 ml kan, CD28 ve CD49d'ye (BD Biosciences) yönelik her bir kostimülatör antikorun 1 µg ml–1 varlığında, 0,6 nmol her bir peptit ile 37 °C'de, %5 CO2'de 6 saat boyunca inkübe edilmiştir. İnkübasyonların başlamasından 2 saat sonra 10 µg ml–1 Brefeldin A (Sigma) ve 2 µg ml–1 monensin (GolgiStop; BD) eklenmiştir. Pozitif kontrol olarak, hücreler 2 µg ml–1 SEB (Sigma) ile inkübe edilmiş ve peptitsiz 3–6 örnek her testte arka plan kontrolü olarak hizmet etmiştir. Stimülasyonu takiben kan 10 dakika boyunca 2 mM EDTA ile muamele edilmiş ve eritrositler RBC lizis tamponu (BioLegend) ile lizize edilmiştir. Hücreler yıkanmış ve virüse özgü T hücreleri daha sonra hücre içi sitokin boyama ile tanımlanmıştır. Bunun için hücreler yüzey antikorları ile etiketlenmiş, ardından Cytofix/Cytoperm Kiti (BD) kullanılarak fikse edilmiş ve permeabilize edilmiş, hücre içi sitokinlere karşı antikorlarla etiketlenmiş ve hemen akış sitometrisi ile analiz edilmiştir. Yüzey antijenleri için şu antikorlar kullanılmıştır: anti-CD3-APC-H7 (1:50), anti-CD4-FITC (1:30), anti-CD8-Pacific Blue (1:100), anti-CD14-PE-Cy7 (1:100) ve anti-CD19-PE-Cy7 (1:50); ve hücre içi boyama için anti-IL-2-Brilliant Violet 510 (5344.111; BD, 1:20), anti-IFNγ-APC (B27; BD, 1:100) ve anti-TNF-PE (Mab11; BD, 1:200). Spesifik olmayan bağlanmanın giderilmesi için 3 mg ml–1 saflaştırılmış insan immünoglobulini (CSL Behring) eklenmiştir. Lenfositler, çift ayrımı ve karakteristik ileri ve yan saçılma özelliklerine göre kapılanmıştır. CD8 veya CD4 T hücreleri, CD14 ve CD19 için negatif (monositleri ve B hücrelerini hariç tutar) ve CD3 ve CD8 veya CD4 için pozitif hücreler seçilerek tanımlanmıştır. Örnek başına 100.000 ile 500.000 arasında CD4 veya CD8 T hücresi olayı toplanmıştır.
Virüse özgü CD8 T hücresi degranülasyon testi
PBMC stimülasyonları, 1 ml başına 10^6 yoğunluğundaki PBMC'lerin 5,5 saat boyunca inkübe edilmesi ve Brefeldin A ile monensinin, inkübasyonun başlangıcında anti-CD107a-PerCP-Cy5.5 (H4A3; BioLegend, 1:200) ile birlikte eklenmesi dışında tam kan için tarif edildiği gibi gerçekleştirilmiştir. Akış sitometrisi analizi için şu ek antikorlar kullanılmıştır: anti-CD3-APC-H7 (1:50), anti-CD8-Pacific Blue (1:100), anti-CD14-PE-Cy7 (1:100), anti-CD16-FITC (3G8; BD, 1:50), anti-CD19-PE-Cy7 (1:50), anti-CD56-FITC (MEM-188; BioLegend, 1:50), anti-IFNγ-APC (1:100) ve anti-TNF-PE (1:200). CD8 T hücreleri, CD14, CD16, CD19 ve CD56 için negatif (monositleri, B hücrelerini ve NK hücrelerini hariç tutar) ve hem CD3 hem de CD8 için pozitif hücreler seçilerek tanımlanmıştır. Örnek başına 20.000 ile 50.000 arasında CD8 T hücresi olayı toplanmıştır.
KIR genotipleme
KIR tiplemesi, DKMS Life Science Laboratory'de geliştirilen kurum içi yüksek verimli bir yaklaşım kullanılarak gerçekleştirilmiştir79. Illumina dizileyicilerinden elde edilen kısa amplikonlar kullanılarak, hedeflenen diziler 3, 4, 5, 7, 8 ve 9 numaralı ekzonları kapsamıştır. Kalibre edilmiş okuma sayılarına dayanarak, kopya sayısı ve allelik varyantlar, IPD-KIR veritabanına referansla ekzon başına belirlenmiştir. Nihai sonuçlar, farklı KIR genleri aynı ekzonik dizileri paylaştığında gen köprüleme durumlarının çözülmesiyle elde edilmiştir. Belirsiz durumlarda bilgi kaybını önlemek için, sonuçlar GL-string'leri78 kullanılarak rapor edilmiştir.
NK hücresi zenginleştirme ve hücre kültürü
NK hücreleri, üreticinin protokolüne göre EasySep Human NK Cell Enrichment Kit (Stemcell Technologies) kullanılarak negatif seçilim stratejisiyle PBMC'lerden zenginleştirilmiştir. İzole edilen NK hücreleri, %10 (v/v) fetal sığır serumu (R10), %1 penisilin-streptomisin (Sigma Aldrich) ve %1 GlutaMAX (Gibco) ile desteklenmiş RPMI içinde kültüre edilmiştir. Belirtilen yerlerde, sadece 1 ng ml−1 IL-15 (Peprotech) veya 50 U ml–1 IL-2 (Novartis) ile kombinasyon halinde eklenmiştir. NK hücreleri daha sonra %5 CO2'de 37 °C'de gece boyunca kültüre edilmiştir. Raji hücreleri, %1 GlutaMAX ve %1 penisilin-streptomisin içeren R10 içinde kültüre edilmiştir.
NK hücrelerinin fenotiplemesi
HIV-1 negatif donörlerden (N = 7) ve donör B2'den alınan dondurulmuş PBMC'ler, 4 °C'de karanlıkta 10 dakika Zombie Aqua Fixable Viability Kit (BioLegend, 1:50) ile boyandıktan sonra oda sıcaklığında 10 dakika insan Fc-bloğu (BD Bioscience, 1:50) ile inkübe edildikten sonra iki panele ayrılmıştır. KIR ifadesini analiz etmek için (panel A), PBMC'ler anti-KIR3DL1-FITC (DX9; BioLegend, 1:100), anti-KIR2DL1-APC Vio770 (REA284; Miltenyi Biotec, 1:25), anti-CD3-AF700 (UCHT1; BD Bioscience, 1:100), anti-NKG2C-APC (REA205; Miltenyi Biotec, 1:100), anti-CD56-BV786 (NCAM16.2; BD Bioscience, 1:100), anti-KIR2DL2/DL3-biotin (DX27, Miltenyi Biotec, 1:10), anti-CD14-BV510 (M5E2; BioLegend, 1:50), anti-CD19-BV510 (HIB19; BioLegend, 1:50), anti-CD57-pacific blue (HNK-1; BioLegend, 1:100), anti-NKG2A-PE-Cy7 (Z199; Beckman Coulter, 1:100) ve anti-KIR3DL1/DS1-PE (REA168; Miltenyi Biotec, 1:50) ile boyanmıştır. Adaptif NK hücresi alt gruplarını analiz etmek için (panel B), PBMC'ler anti-CD7-PerCP-Cy5.5 (4H9/CD7; BioLegend, 1:100), anti-Siglec7-APC-Vio770 (REA214; Miltenyi Biotec, 1:25), anti-CD2-AF700 (RPA-2.10; BioLegend, 1:100), anti-NKG2C-APC (REA205; Miltenyi Biotec, 1:100), anti-CD16-BV785 (3G8; BioLegend, 1:100), anti-ILT2-biotin (REA998; Miltenyi Biotec, 1:50), anti-CD161-BV605 (HP-3G10; BioLegend, 1:100), anti-CD8-BV570 (RPA-T8; BioLegend, 1:100), anti-CD14-BV510 (M5E2; BioLegend, 1:50), anti-CD19-BV510 (HIB19; BioLegend, 1:50), anti-CD57-pacific blue (HNK-1; BioLegend, 1:100), anti-NKG2A-PE-Vio770 (REA110; Miltenyi Biotec, 1:100), anti-CD56-BUV737 (NCAM16.2; BD Bioscience, 1:100) ve anti-CD3-BUV395 (UCHT1; BD Bioscience, 1:100) ile boyanmıştır.
Her iki panelden biriyle boyanan hücreler 4 °C'de karanlıkta 30 dakika inkübe edilmiş, %1 FBS–PBS ile iki kez yıkanmış ve ardından 4 °C'de karanlıkta 20 dakika Streptavidin BV711 (BioLegend, 1:200) ile inkübe edilmiştir. %1 FBS–PBS ile iki kez yıkandıktan sonra, panel A ile boyanan hücreler fikse edilmemiş halde bırakılmış ve hemen BD FACSAria kullanılarak analiz edilmiştir. Panel B için hücre içi boyama, üreticinin protokolüne göre anti-FcεR1γ-FITC (poliklonal, Merck, 1:50) ve anti-PLZF-PE (Mags.21F7; eBioscience, 1:100) ile birlikte BD Cytofix/Cytoperm Fiksasyon/Permeabilizasyon Kiti (BD Biosciences) kullanılarak gerçekleştirilmiştir. Hücreler yıkanmış ve Cytek Aurora akış sitometresinde analiz edilene kadar 4 °C'de %1 FBS–PBS içinde saklanmıştır.
Rituximab'a yanıt olarak degranüle olan hasta B2'nin NK hücresi alt gruplarının fenotiplemesi için, hücreler önce 4 °C'de karanlıkta 10 dakika Zombie Aqua Fixable Viability Kit (BioLegend, 1:50) ile inkübe edilmiştir. Yıkamadan sonra, yüzey boyama 4 °C'de karanlıkta 20 dakika boyunca şu antikorlar kullanılarak gerçekleştirilmiştir: anti-NKG2C-APC (REA205; Miltenyi Biotec, 1:100), anti-NKG2A-PE Vio770 (REA110; Miltenyi Biotec, 1:100), anti-CD16-BV785 (3G8; BioLegend, 1:100), anti-Siglec7-APC-Vio770 (REA214; Miltenyi Biotec, 1:25), anti-CD7-PerCP-Cy5.5 (4H9/CD7; BioLegend, 1:100), anti-CD56-BUV395 (NCAM16.2; BD Biosciences, 1:100), anti-KIR3DL1-AF700 (DX9; BioLegend, 1:100), anti-KIR2DL2/DL3-BV711 (DX27; BD Biosciences, 1:50), anti-KIR2DL1-PE (HP-DM1; BioLegend, 1:50) ve anti-CD57-PE Dazzle 594 (HNK-1; BioLegend, 1:100). Daha sonra hücreler %1 FBS–PBS ile iki kez yıkanmış, 1× CellFIX (BD Biosciences) ile fikse edilmiş ve Cytek Aurora akış sitometresinde analiz edilmiştir. Hasta B2'den alınan plazmanın aktivitesini değerlendirmek için immobilize Env kullanılan ADCC testi için, NK hücreleri oda sıcaklığında 20 dakika boyunca Live/Dead Fixable Near-IR Dead Cell Stain Kit (Invitrogen, 1:1.000) ile anti-CD16 BV711 (3G8; BioLegend, 1:100) ve anti-CD56 BUV395 (NCAM16.2; BD Biosciences, 1:100) ile inkübe edilmiştir. Boyamadan sonra hücreler %1 FBS içeren PBS ile iki kez yıkanmış, %4 paraformaldehit (Sigma-Aldrich) ile fikse edilmiş ve LSR Fortessa akış sitometresi (BD Biosciences) kullanılarak analiz edilmiştir. Akış sitometrisi verileri, UMAP ve FlowSOM eklentisi ile FlowJo (v.10.8.1; BD Life Sciences) kullanılarak analiz edilmiştir.
NK hücrelerinin boyutsallık azaltma analizi
Akış sitometrisi verileri (panel B), boyutsallık azaltma analizine tabi tutulmadan önce R'de (v.4.4.1) NK hücreleri üzerinde kapılanmıştır. Analiz, halka açık olarak mevcut olan R paketi Seumetry (v.0.1.0)81 temel alınarak yapılmıştır. Hasta B2'den ve yedi HIV negatif bireyden (kontrol grubu olarak) alınan Fcs dosyaları bir flowset içinde birleştirilmiş ve ardından donör başına yaklaşık 20.000 hücreye düşürülüp arcsinh transformasyon yöntemi kullanılarak transforme edilmeden önce bir Seurat nesnesine dönüştürülmüştür. Aykırı değerler manuel olarak kaldırıldıktan, veriler ölçeklendirildikten ve temel bileşen analizi yapıldıktan sonra, ilk on temel bileşene dayalı bir UMAP oluşturulmuştur. Nihai NK hücresi kümeleri, Louvain algoritması kullanılarak tanımlanmış ve ardından benzer kimliklere sahip kümeler birleştirilmiştir.
ADCC testleri
Hasta B2'den farklı NK hücresi alt gruplarının ADCC kapasitesini değerlendirmek için, zenginleştirilmiş NK hücreleri %1 penisilin-streptomisin, %1 GlutaMAX ve 1 ng ml–1 IL-15 ile desteklenmiş R10 içinde gece boyunca kültüre edilmiştir. Ertesi gün hücreler U-tabanlı 96 kuyulu bir plakaya aktarılmıştır. Ortak inkübasyondan önce Raji hücreleri, 4 dakika sonra karıştırılarak oda sıcaklığında 1 ml PBS içinde 8 dakika boyunca CFSE (1:2.000) ile inkübe edilerek floresan boya CFSE (Invitrogen) ile etiketlenmiştir. Reaksiyon 7 ml %10 FBS–RPMI kullanılarak durdurulmuştur. Daha sonra Raji hücreleri (ml başına 10^6 hücre), 30 µg ml–1 rituximab (Invivogen) ile %5 CO2'de 37 °C'de 30 dakika boyunca kaplanmıştır. Kaplanmamış Raji hücreleri kontrol olarak kullanılmıştır. NK ve Raji hücreleri, anti-CD107a-BV421 (H4A3, BioLegend, 1:100) varlığında %5 CO2'de 37 °C'de 3,5 saat boyunca 2:1 E:T oranında ortak kültüre edilmiştir. Ortak kültürden sonra hücreler akış sitometrisi analizi için boyanmıştır (bkz. 'NK hücrelerinin fenotiplemesi' bölümü). Hasta B2'den alınan plazmanın indüklediği ADCC aktivitesini değerlendirmek için, Env proteini doku kültürü uygulanmamış, düz tabanlı 96 kuyulu plakalara (Corning) immobilize edilmiştir. Kuyular ya 10 µg ml–1 HIV-1 Ba-L_01 gp120 proteini (Sino Biological) ile 4 °C'de gece boyunca kaplanmış ya da kaplanmamış bırakılmıştır (kontrol olarak sadece PBS). Ertesi gün kuyular PBS ile üç kez yıkanmış ve 4 °C'de gece boyunca PBS içinde %2 BSA (Sigma-Aldrich) ile bloklanmıştır. Bloklamadan sonra kuyular PBS ile yıkanmış ve 4 °C'de 45 dakika boyunca kuyu başına 60 µl olmak üzere şunlardan biriyle inkübe edilmiştir: 1–18, VRC01 ve 10–1074 dahil olmak üzere PBS içinde üç geniş nötralize edici antikorun 10 µg ml−1'i; beş elite kontrolcüden ve hasta B2'nin beş boylamsal zaman noktasından 1:1.000 PBS seyreltilmiş plazma örnekleri; HIV negatif bir bireyden 1:1.000 PBS seyreltilmiş plazma; veya sadece PBS (negatif kontrol). Kuyular daha sonra PBS ile iki kez yıkanmıştır. Heterolog HIV-1 negatif donörlerden alınan PBMC'ler testten 1 gün önce izole edilmiş, NK hücreleri zenginleştirilmiş ve %1 penisilin-streptomisin, %1 GlutaMAX, 1 ng ml–1 IL-15 ve 50 U ml–1 IL-2 ile desteklenmiş R10 içinde gece boyunca kültüre edilmiştir. Daha sonra 105 NK hücresi, 100 µl hacimde kaplanmış kuyulara eklenmiş, 300g'de 3 dakika (3 hızlanma ve yavaşlama ayarları) santrifüj edilmiş ve anti-CD107a BV421 antikor (H4A3; BioLegend, 1:100) varlığında %5 CO2 ile 37 °C'de 4 saat boyunca inkübe edilmiştir. İnkübasyonun ardından kuyular, NK hücrelerini ayırmak için MACS tamponu (Miltenyi Biotec) ile iyice yıkanmış ve hücreler akış sitometrisi analizi için 96 kuyulu U-tabanlı plakalara aktarılmıştır (bkz. 'NK hücrelerinin fenotiplemesi' bölümü).
Geri tepme zamanı ve olasılığı modelleri
Önceki bir çalışma35, AIDS Klinik Deney Grubu (ACTG) çalışmalarından (371, A5024, A5068, A5170, A5187 ve A5197) N = 235 ATI katılımcısından oluşan büyük bir kohorttan gelen verileri kullanarak hem kısa vadeli hem de uzun vadeli viral geri tepmeleri açıklayan, mekanistik olarak motive edilmiş, fenomenolojik bir model tanımlamıştır35.
Dahil edilme kriterleri, HIV-1 RNA'nın <50 kopya/ml olduğu ve katılımcıların başka hiçbir immünolojik müdahale almadığı baskılayıcı ART'dir. Bireylerin çeşitliliğini, ATI'den aylar sonra geri tepen bazılarını içerecek şekilde uygun şekilde modellemek için, yazarlar dikkatli bir model seçim teorisi uygulamış ve yeniden aktivasyon oranının erken bir orandan (r0) uzun vadeli bir orana (r∞) zamanla azaldığı, hala parçalı bir fonksiyon olan bir modele ulaşmışlardır:
$$r(s)=0\,\mathrm{when}\,s\le \tau $$
(1)
$$r(s)={r}_{\infty }+({r}_{0}-{r}_{\infty })\exp [-k\times (s-\tau )],{\rm{else}}$$
(2)
Geri tepme olasılığının zaman içindeki bu fonksiyonun kümülatif olasılığının üstel değerine bağlı olduğu tipik bir tehlike fonksiyonu varsayımıyla, nihai geri tepme olasılığı (Şekil 5a'da gösterildiği gibi) şöyle yazılır:
$$P(t)=1-\exp \left[-{\int }_{\tau }^{t}r(s){\rm{d}}s\right]$$
(3)
Bu ve diğer veri onaylı yaklaşımlarda, modelin yaklaşık 5 günlük bir gecikme gerektirdiğini, böylece geri tepme olasılığı fonksiyonu \({p}_{\mathrm{VR}}\) değerinin gecikme süresinden (\(\tau \)) önce sıfır olduğu parçalı bir fonksiyon olarak tanımlandığını unutmayın. Bu fonksiyonu, \(y > 0\) olduğunda değeri 1 ve aksi takdirde 0 olan bir Heaviside basamak fonksiyonu \(\Theta (y)\) kullanarak not etmeyi seçtik. Bu nedenle, genel zamana bağlı geri tepme olasılığını yazdık.
$${p}_{\mathrm{VR}}(t)=\Theta (\tau -t)P(t)$$
(4)
Burada \(P(t)\), gecikme süresinden sonra geri tepmeyi yöneten fonksiyondur, burada denklem (3).
Tahmini parametreler ortalama ve (%95 CI) değerleriyle şöyledir: gün başına r0 = 0,088 (0,073, 0,106), gün başına r∞ = 0,002 (0,001, 0,004), gün başına k = 0,029 (0,022, 0,040) ve τ = 4,98 (4,58, 5,41) gün.
Hasta ATI'miz için bu parametreleri denklem (4)'te t = 6 yıl olarak değerlendirerek geri tepmeme olasılığını hesapladık.
Daha sonra, sabit bir nüks oranına sahip daha klasik bir viral geri tepme modeli aldık ve heterozigot CCR5Δ32'ye sahip bu HCT hastası için tüm dönem boyunca geri tepme olmadığını açıklamak için hangi değerlerin (\({r}_{\Delta \pm }\) sabit oranı) gerekeceğini araştırdık. \({r}_{\Delta \pm }\) değerini, 6 yılda %5, 50 ve 95 geri tepme şansı üreten değerleri çözerek tahmin ettik, yani \(\mathrm{ln}(1-P)/-6\,\mathrm{year}={r}_{\Delta \pm }.\)
Veri sunumu
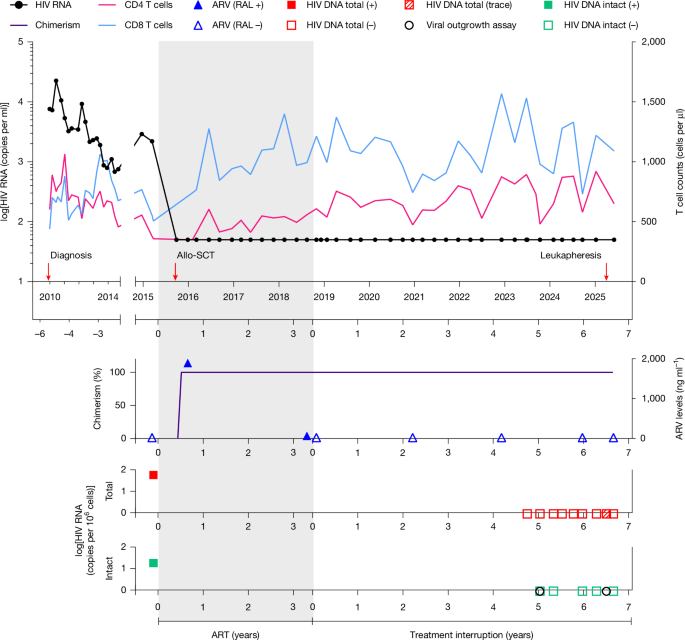
Veri şekilleri Affinity Designer ve Adobe Illustrator'da düzenlenmiştir. Maksimum olabilirlik filogenisi FigTree (v.1.4.4) kullanılarak görselleştirilmiştir.
Raporlama özeti